- Accueil
- Actualités
- Première Observation de Structures Inhabituelles de L’ADN Chez Les Archées
Première observation de structures inhabituelles de l’ADN chez les archées
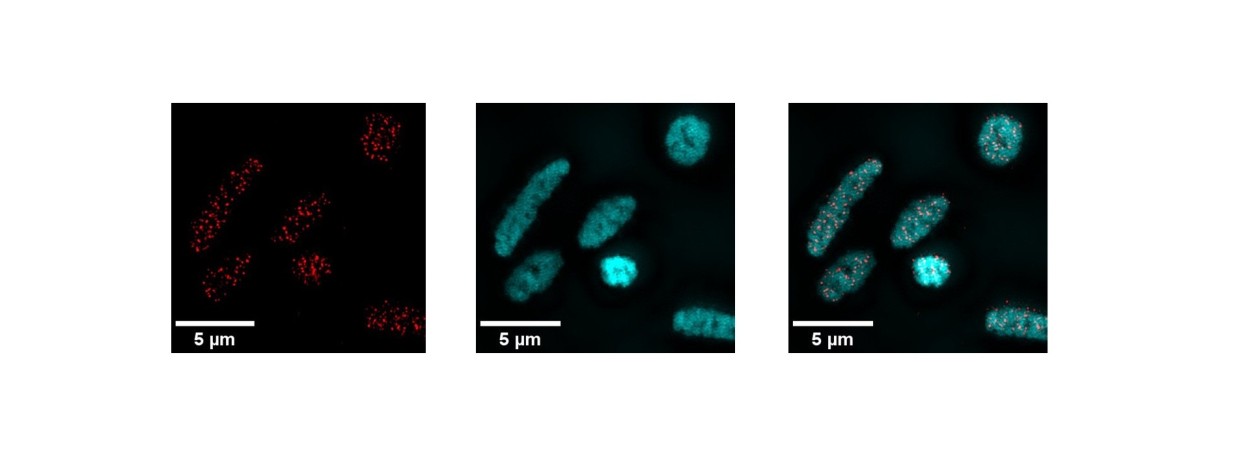 Détection en microscopie à super-résolution, chez Haloferax volcanii, des structures G-quadruplexes (rouge), de l’ADN (cyan) et leur superposition.
Détection en microscopie à super-résolution, chez Haloferax volcanii, des structures G-quadruplexes (rouge), de l’ADN (cyan) et leur superposition.
La double hélice est célèbre comme symbole du génome. C’est en effet sous cette forme que l’ADN se trouve dans les cellules des êtres vivants. Du moins, en majorité. Car, derrière cette norme de la double hélice, se cache une diversité de structures inhabituelles des brins d’acides nucléiques (les fameuses bases A, C, G, T). Les scientifiques estiment qu’environ 13% du génome d’une cellule humaine pourrait s’assembler différemment.
Les G-quadruplexes en particulier font partie de ces alternatives. Ils sont formés de bases de guanine (G), qui s’assemblent par quatre selon un plan. « Ces plans peuvent s’empiler et créer différentes configurations de molécule ADN, soit avec quatre brins, deux brins ou même un seul brin » explique Lionel Guittat, enseignant-chercheur à l’université Sorbonne Paris Nord et membre du LOB.
Microscopie à super-résolution
« Beaucoup de travail d’identification de G-quadruplexes a déjà été fait sur des cellules eucaryotes comme celles des mammifères, mais rien sur les archées » poursuit le biologiste. Or les archées sont très intéressantes. Ce sont des espèces monocellulaires, comme les bactéries, mais des études génomiques récentes (notamment grâce au séquençage massif) ont révélé que les eucaryotes partagent une parenté plus étroite avec les archées qu’avec les bactéries. Il semble que les eucaryotes trouvent leurs origines dans une fusion entre une archée et une bactérie.
Lionel Guittat et son équipe, notamment Kate Sorg et Zackie Aktary, ont identifié pour la première fois les G-quadruplexes (G4) dans les archées. Plus précisément chez l’espèce Haloferax volcanii, cultivée au LOB.
D’abord, un algorithme d’identification, à partir du génome séquencé de l’organisme, a analysé dans la succession de bases des potentiels sites de G4 et en a repéré plus de 5000. Surtout, les scientifiques ont réussi à en visualiser. Pour cela, des anticorps spécifiquement connus pour pouvoir s’attacher aux G4 ont été introduits dans des cellules d’Haloferax volcanii. Cet anticorps était lui-même lié à une molécule fluorescente, c’est-à-dire qu’elle s’illumine quand on l’éclaire de façon adéquate.
Ainsi, grâce à de la microscopie par fluorescence à super-résolution SIM (Structured Illuminated Microscopy) capable de distinguer des détails de 100 nanomètres, l’équipe a réussi à voir les G4 au sein des archées. « Nous avons effectué plusieurs contrôles afin de comprendre ce que nous observions exactement. Notamment, si on ajoute une protéine qui dégrade l’ADN, on n’observe plus de signal. Cela signifie que notre expérience met bien en évidence des structures de l’ADN » souligne Lionel Guittat. Une autre expérience montre que les G4 sont également présent sur l’ARN des archées.
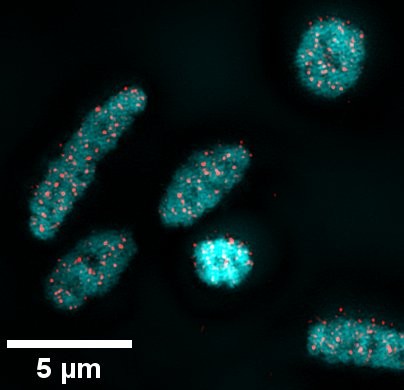
Comprendre la fonction des G4
En poussant plus loin l’étude par une approche d’imagerie de super-résolution STORM (Stochastic Optical Reconstruction Microscopy), Kate Sorg a pu quantifier plus précisément le nombre de G4 que l’on peut ainsi detecter dans une cellule d’Haloferax Volcanii : une cinquantaine.
Ces résultats ont aussi été confirmés sur une autre espèce d’archée, Thermococcus barophilus, en collaboration avec l’équipe Biologie de l’ARN chez les Archées (MCD – CBI) de l’université de Toulouse. Après cette première, les chercheuses et chercheurs s’attèlent déjà à la suite : identifier les séquences précises du génome des archées où se trouvent les G4 observés et en savoir plus sur leur fonction. « On sait que les G4 peuvent inhiber ou au contraire activer la duplication de l’ADN, sa transcription en ARN ou encore la traduction en protéines, mais cela reste à comprendre, en particulier chez les archées » confie Lionel Guittat.
Référence :
Zackie Aktary, Kate Sorg et al., Archaeal G-quadruplexes: a novel model for understanding unusual DNA/RNA structures across the tree of life, Nucleic Acids Research, Volume 54, Issue 4, 27 February 2026, gkag067, https://doi.org/10.1093/nar/gkag067
*LOB : une unité mixte de recherche CNRS, Inserm, École polytechnique, Institut Polytechnique de Paris, 91120 Palaiseau, France
 Je soutiens l'X
Je soutiens l'X